搜索结果: 1-7 共查到“计算机软件 蛋白质”相关记录7条 . 查询时间(0.261 秒)
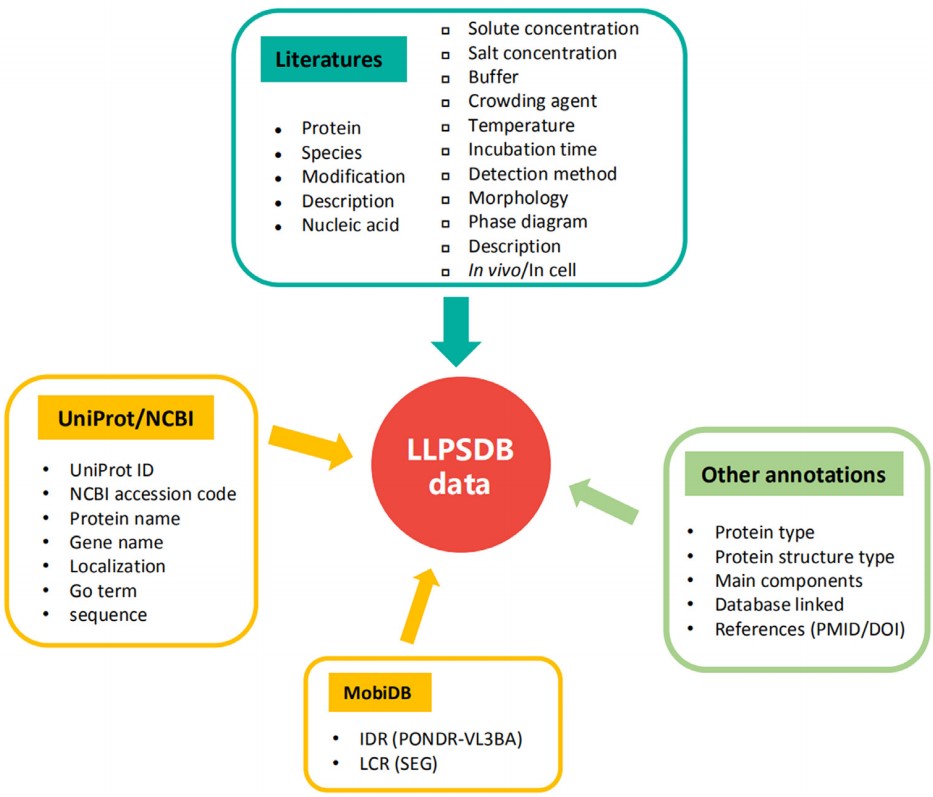
近年来,蛋白质液液相分离(Liquid-liquid Phase Separation, LLPS)逐渐成为生物学研究的热点之一。它在生命体的正常代谢和疾病过程中都发挥着非常重要的作用。随着越来越多的探索LLPS具体发生机制的报道,人们发现影响蛋白质LLPS的因素主要来自于两个方面:一是蛋白质序列性质,如突变及翻译后修饰的影响;二是受到体系微环境,比如温度、蛋白质浓度、pH值、盐浓度、压力等的调节...
GridMol系统中蛋白质可视化与建模的性能优化
分子建模 性能分析 GridMol系统
2009/10/20
基于网格计算思想开发一个具有计算化学前、后处理功能的系统GridMol,其主要功能包括分子可视化、分子建模和计算作业提交。针对GridMol系统中蛋白质大分子显示和建模遇到的性能问题,给出调整Java 3D场景图进行性能优化的方法,通过GridMol和其他分子可视化软件的性能比较以及自身优化前后的性能比较,证明优化方法取得了良好的效果。
一种新的蛋白质序列模式挖掘算法
模式挖掘 数据挖掘 生物信息学
2009/8/17
针对传统模式挖掘方法挖掘蛋白质序列会生成大量候选模式或多次构造投影数据库,导致效率降低,挖掘过程中会产生不必要的短模式或错误模式等问题,提出基于模式划分的MBioPM算法。理论分析和实验表明,MBioPM算法的性能高于其他相关算法。
基于蛋白质CGR的线粒体蛋白质序列比对
蛋白质混沌游走表示法 蛋白质序列比对 氨基酸分类
2009/7/17
利用蛋白质混沌游走表示法(PCGR)提出一种新的蛋白质序列比对方法。通过计算两序列之间的PCGR点距离,就可以找到所有的局部相似片断。根据氨基酸的化学物理性质把氨基酸分成4和7类,针对分类与无分类的各种情况进行蛋白质序列比对。为了更直观地描述比对结果,采用点阵图来表示比对数据,不仅能显示两序列间所有相同片断,还可以体现出序列的相似性。
基于蛋白质相互作用网络的聚类算法研究
聚类算法 网络距离 最短路径
2009/7/17
蛋白质相互作用网络是计算机科学技术的一个新研究领域。蛋白质相互作用网络中结点之间的距离度量需要通过基于网络的最短路径距离来重新定义,其计算代价高,这使得已有的基于欧几何距离的聚类算法不能直接运用到这种环境中。因此,通过蛋白质相互作用网络的特征提出了一种新的聚类算法。算法使用网络中的边和结点信息来缩减搜索空间,避免了一些不必要的距离计算。实验结果表明,算法对于真实的蛋白质相互作用网络中的结点聚类是高...
基于蛋白质相互作用网络图的聚类方法
算术平均最小值 K-means聚类方法 准则函数
2009/7/17
依据人类AD(Alzheimer’s Disease)相关蛋白质相互作用网络图,利用基于算术平均最小值――AAMV(Arithmetic Average Minimum Value)的K-means聚类方法对蛋白质进行聚类并预测4个孤立蛋白质的功能。分析结果表明:所得结果与用Maryland Bridge 法及Korbel法所得结果非常相似。

